Odkrycie kodu genetycznego znacznie ułatwia przewidywanie konsekwencji mutacji w genach kodujących białka, jednak zdecydowana większość (ok. 99%) wariantów genetycznych w ludzkim genomie występuje poza sekwencjami kodującymi, w różnych regionach „niekodujących”, w tym w genach miRNA, i nadal nie mamy „kodu” pozwalającego przewidzieć ich konsekwencje.
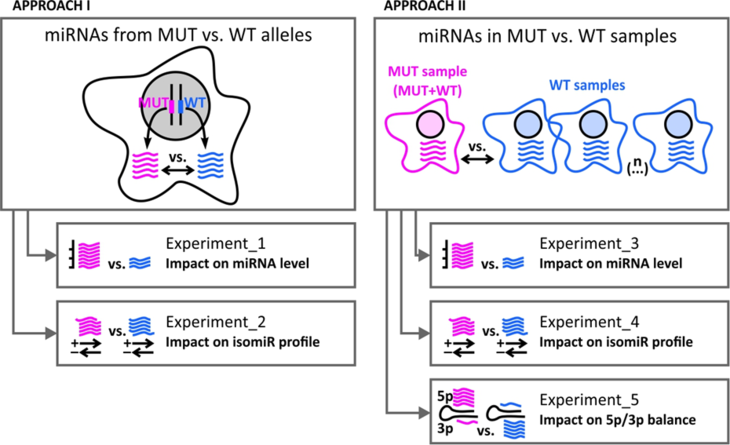
W niniejszym badaniu naukowcy z ICHB PAN przeanalizowali konsekwencje mutacji w genach miRNA, porównując setki mutacji, które wcześniej zidentyfikowali w genomach nowotworowych (Martyna Urbanek-Trzeciak i in., „eBioMedicine”, 2020), z odpowiadającymi im danymi z analizy miRNA-seq. W ten sposób wykazali, że większość mutacji w genach miRNA jest szkodliwa, poważnie upośledzając ich funkcje. Dlatego jeśli występują w genach miRNA związanych z chorobami, mogą być wariantami patogennymi. Badanie wykazało, że mutacje mogą wpływać na:
* poziom miRNA,
* równowagę nici miRNA 5p/3p,
* precyzję cięcia DROSHA/DICER1 (profile isomiR),
* skuteczność wyciszania genów docelowych.
Wykazano również, że skutki mutacji w dużym stopniu zależą od ich wpływu na strukturę prekursora miRNA. Liczba mutacji genów miRNA analizowanych w tym badaniu oraz liczba mutacji o zidentyfikowanych szkodliwych skutkach przewyższyła te uzyskane w innych badaniach funkcjonalnych o rzędy wielkości. Badanie stanowi solidną podstawę do lepszego zrozumienia i przewidywania konsekwencji mutacji wykrytych w genach miRNA.
ICHB PAN
























KOMENTARZE